Gene Silencing
Entdecken Sie die innovative Welt des Gene Silencing! Mit hochspezifischen siPOOLs minimieren Sie Off-Target-Effekte und erzielen ein nahezu optimales Gen-Silencing. Von der Indentification der Genfunktionen bis zur Krankheitsanalyse – unsere fortschrittliche RNAi-Technologie setzt neue Maßstäbe in Effizienz und Zuverlässigkeit. Sparen Sie Zeit und Ressourcen mit dem präzisen Knockdown-Tool für Ihre Forschung.
Wissenswertes zu Gene Silencing
Unter Gene Silencing (Gen-Stilllegung) versteht man die Regulierung/Inaktivierung der Expression eines bestimmten Gens in einer Zelle. Dies kann entweder während oder nach der Transkription erfolgen. Gene Silencing wird oft synonym zu Gene-Knockdown verwendet.
RNA-Interferenz (RNAi) ist ein natürlicher Mechanismus in Zellen vieler Eukaryoten, der zum zielgerichteten Abschalten von Genen führt. Dieser Mechanismus kann durch epigenetische Modifikationen beeinflusst werden. Ausgelöst wird dieser durch kleine, doppelsträngige RNA-Moleküle, die man siRNA (small interfering RNA) nennt. In der Regel sind diese 21 Nukleotide lang.
Als Methode wird RNAi in der Forschung vielfältig zum spezifischen Ausschalten von Genen genutzt. Diese Technologie hat sich bei der Entschlüsselung diverser molekularer Signaltransduktionswegen von biologischen Stoffwechselwegen, der Analyse von Krankheitsgenen und auch in der Pflanzenforschung vielfach bewährt.
siRNAs können so konzipiert werden, dass sie auf bestimmte Gene abzielen. Einzelne siRNAs können jedoch unvorhersehbar sein und an nicht zielgerichtete mRNA-Sequenzen binden (Seed-Effekt), was zu Off-Target-Effekten führt. Off-Target-Effekte können die Genauigkeit von RNAi-Experimenten beeinträchtigen und möglicherweise zu irreführenden Ergebnissen oder unerwarteten Phänotypen führen. Die Minimierung dieser Effekte ist entscheidend für zuverlässige Gene-Knockdown-Studien.
Potent & Specific Gene-Knockdown by RNAi durch siPOOLs
siRNA-Pools (siPOOLs) sind komplexe Pools aus 30 optimal konzipierten siRNAs, die nachweislich effizient Off-Target-Effekte minimieren. Durch die sehr niedrige Konzentration jeder einzelnen siRNA werden off-target Effekte zuverlässig verdünnt. Gleichzeitig wird das Zielgen durch die kooperative Aktivität vieler siRNAs robust stillgelegt. Der proprietäre Design-Algorithmus garantiert die Auswahl potenter siRNAs mit maximaler Transkript-Abdeckung und vermeidet die Verwendung paraloger Zielgen-Bereiche. siPOOLs erzeugen so zuverlässige zelluläre Effekte, die die Spezifität einzelner siRNAs und niedrig komplexer siRNA Mischungen deutlich verbessern.
Vorteile der siPOOLs:
-
Definierter Pool von 30 ausgewählten siRNAs
-
Extrem robuste und effiziente Zielgen Stilllegung
-
Maximale Zielgen-Spezifität
-
Verwendung der aktuellsten NCBI Annotationen des menschlichen Genoms (RefSeq release 214)
-
Gleichmäßig effiziente Stilllegung mehrere Zielgene durch siPOOL Kombinationen
-
Einsparung von Zeit und Geld durch die Vermeidung redundanter Experimente mit multiplen, unspezifischen Einzel-siRNAs.
Hauptproblem beim Gene Silencing: Off-Target-Effekte von siRNAs
Wissenschaftler haben die RNA-Interferenz (RNAi) als schnelles und effizientes Instrument zur Erforschung der Genfunktion eingesetzt. Doch die Off-Target-Effekte und die variable Performance von kurzen interferierenden RNAs (siRNAs) sind nach wie vor ein Nachteil, der wertvolle Zeit und Ressourcen für die Validierungsbemühungen verbraucht.
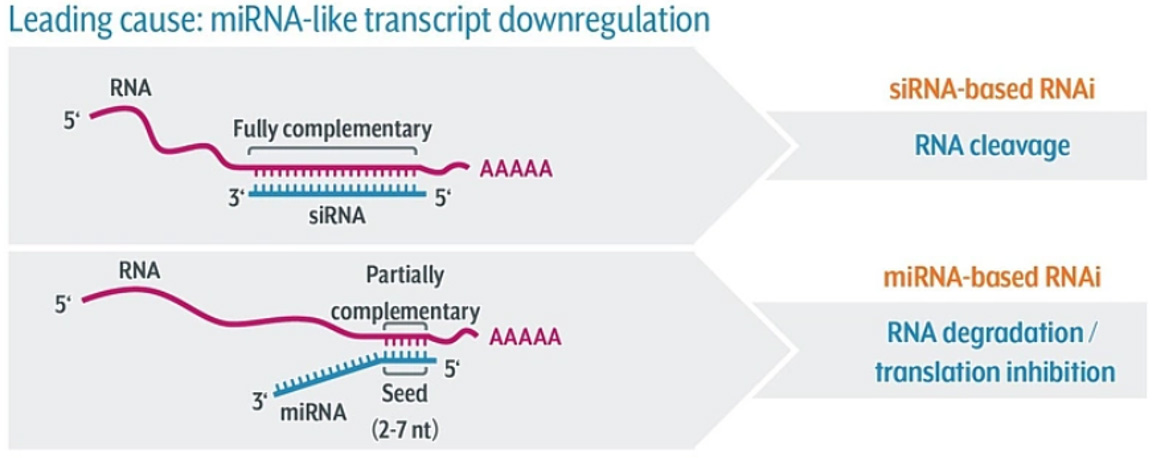
siRNAs binden in der Regel mit voller Komplementarität an Ziel-RNA-Transkripte und führen zu deren Abbau durch die RNAi-Maschinerie. Off-Target-Effekte werden weitgehend durch siRNAs verursacht, die endogene Genregulatoren, Mikro-RNAs (miRNAs), nachahmen. Da miRNAs nur eine 6-Basen-Seed-Sequence mit der 3'-untranslatierten Region (UTR) benötigen, um die Herunterregulierung eines Transkripts auszulösen, können siRNAs so die Expression zahlreicher unbeabsichtigte Gene verändern.
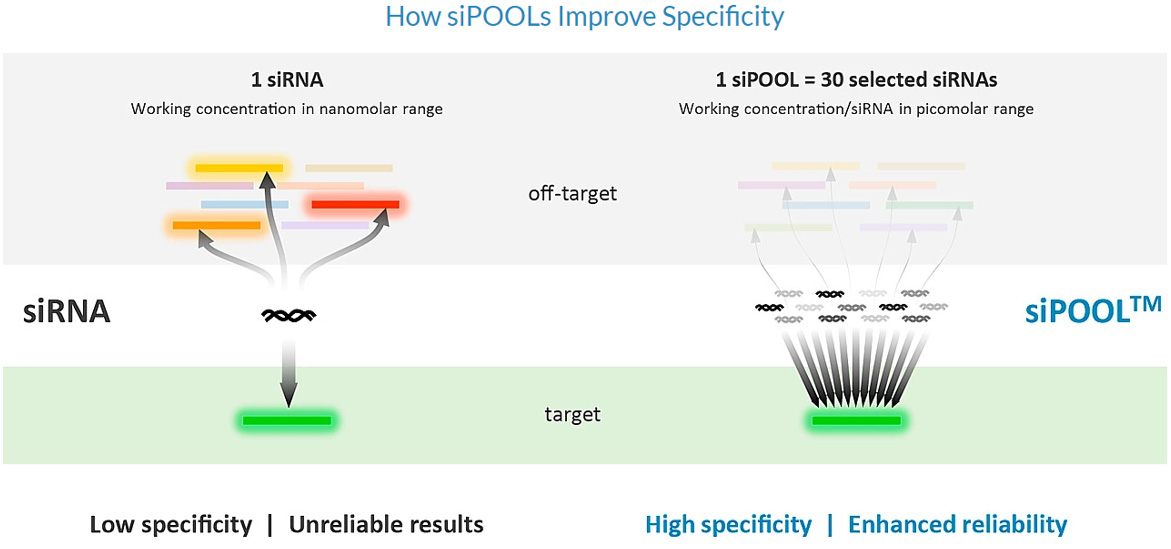
Einzelne siRNAs oder siRNA-Pools von geringer Komplexität, die 3 bis 4 siRNAs enthalten, treffen oft mehrere Off-Target-Gene und zeigen einen variablen Zielgen-Knockdown.
Kurze interferierende RNA-Pools (siPOOLs) sind hochkomplexe und definierte Pools von 30 siRNAs, wobei jede siRNA in einer picomolaren Arbeitskonzentration vorliegt.
Dies:
-
Schwächt die Off-Target-Signatur jeder siRNA ab und erhöht die On-Target-Spezifität.
-
Gewährleistet einen kooperativen Knockdown des Zielgens, was zu robusteren und zuverlässigeren Ergebnissen führt.
Optimiertes und detailliertes siRNA-Design
Mit definierten siRNA-Sequenzen innerhalb des siPOOLs kann das Targeting gegen bestimmte Transkript-Isoformen oder eng verwandte Gene optimiert werden. Proprietäre siRNA-Design-Algorithmen wählen die wirksamsten siRNAs auf der Grundlage thermodynamischer Eigenschaften aus, die die Ladung des Leitstrangs in den RNA-induzierten Silencing-Komplex (RISC) begünstigen. Unter Verwendung der neuesten RefSeq-Annotationen und genomweiter Paralog-Filterung werden siPOOLs für eine maximale Abdeckung aller Zieltranskripte mit hoher Spezifität entwickelt.
Übrigens: Biozym bietet auch Produkte zur RNA-Aufreinigung an, die für Gene Silencing-Experimente unerlässlich sind. Eine effiziente RNA-Aufreinigung ist entscheidend, um qualitativ hochwertige RNA für nachfolgende Silencing-Experimente zu erhalten.
FAQ: Häufig gestellte Fragen zum Thema Gene Silencing
Was ist der Unterschied zwischen den siPOOLs und den anderen im Handel erhältlichen siRNA-Pools?
Bei anderen im Handel erhältlichen siRNA-Pools handelt es sich entweder um wenig komplexe Pools mit 3-4 siRNAs oder um stochastische Pools mit unterschiedlichen siRNA-Längen. Im Gegensatz dazu sind siPOOLs die ersten verfügbaren hochkomplexen Pools aus sorgfältig ausgewählten siRNAs mit definierter Länge.
Können siPOOLs kombiniert werden, um mehrere Gene gleichzeitig auszuschalten?
Ja. siPOOLs sind bei niedrigen pikomolaren Konzentrationen effizient. Daher können mehrere siPOOLs in einer einzigen Anwendung kombiniert werden, um mehrere Gene bei minimalem Risiko von Nebenwirkungen auszuschalten.
Welcher siPOOL wird als Negativkontrolle verwendet?
Wir verwenden einen Standard-Negativkontroll siPOOL (30 siRNAs), der nicht mit Genen von Mensch, Maus und Ratte interagiert. Dieser wurde an mehreren Zelllinien getestet und zeigt keine signifikanten Auswirkungen auf Zellproliferation, Zelltod oder Zellmorphologie. Auf Anfrage können auch „scramble“* negative Kontroll-siPOOLs geliefert werden, um eine Interaktion mit dem Ziel zu vermeiden, während der %GC-Gehalt erhalten bleibt.
*eine „scramble“ siRNA hat die gleiche Nukleotid-Zusammensetzung, aber nicht die gleiche Sequenz wie die Test-siRNA.







